案例数据:
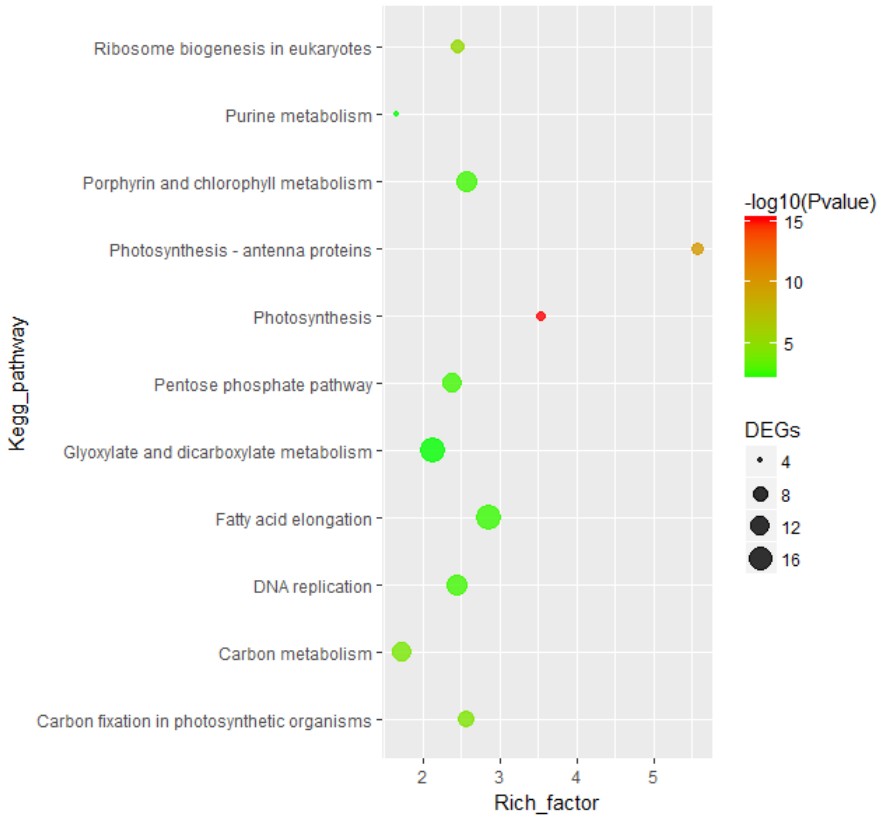
> dat ko_id Kegg_pathway Rich_factor Pvalue DEGs1 ko00195 ...
Pathway富集结果常用气泡图来显示,其基本代码如下:
案例数据:
> dat
ko_id Kegg_pathway Rich_factor Pvalue DEGs
1 ko00195 Photosynthesis 3.543363 1.000000e-15 5
2 ko00196 Photosynthesis - antenna proteins 5.575221 1.500000e-10 6
3 ko03008 Ribosome biogenesis in eukaryotes 2.464696 4.920000e-06 7
4 ko00710 Carbon fixation in photosynthetic organisms 2.567654 4.510000e-05 9
5 ko01200 Carbon metabolism 1.738592 7.350000e-05 11
6 ko03030 DNA replication 2.453097 1.772599e-03 14
7 ko00030 Pentose phosphate pathway 2.397575 1.772599e-03 12
8 ko00860 Porphyrin and chlorophyll metabolism 2.574238 1.772599e-03 14
9 ko00062 Fatty acid elongation 2.857551 2.316650e-03 18
10 ko00630 Glyoxylate and dicarboxylate metabolism 2.129425 5.299956e-03 19
11 ko00230 Purine metabolism 1.671398 5.299956e-03 4
绘图常利用geom_point几何对象函数实现气泡图绘制过程,同时实现坐标轴翻转
注意显著性大小-log10(Pvalue)映射到的点颜色上、差异基因数映射到点大小上。
kegg_point=ggplot(dat,aes(x=Kegg_pathway,y=Rich_factor))+
geom_point(aes(color=-log10(Pvalue),size=DEGs),alpha=0.8)+
coord_flip()+
scale_color_gradient(low = "green",high = "red")
kegg_point
 不过需要注意的是在部分情况下,对应的DEGs数量较小,自动匹配的点的大小较小,在图片上难以显示明显,可以利用scale_size_continuous(range)参数控制,
不过需要注意的是在部分情况下,对应的DEGs数量较小,自动匹配的点的大小较小,在图片上难以显示明显,可以利用scale_size_continuous(range)参数控制,
kegg_point=kegg_point+scale_size_continuous(range=c(4,10))
kegg_point
size对应的range参数可以有效控制点大小的范围。
1. 文章越来越难发?是你没发现新思路,基因家族分析发2-4分文章简单快速,学习链接:
基因家族分析实操课程
、
基因家族文献思路解读
2. 转录组数据理解不深入?图表看不懂?点击链接学习深入解读数据结果文件,学习链接:
转录组(有参)结果解读
;
转录组(无参)结果解读
3. 转录组数据深入挖掘技能-WGCNA,提升你的文章档次,学习链接:
WGCNA-加权基因共表达网络分析
4. 转录组数据怎么挖掘?学习链接:
转录组标准分析后的数据挖掘
、
转录组文献解读
5.
微生物16S/ITS/18S分析原理及结果解读
、
OTU网络图绘制
、
cytoscape与网络图绘制课程
6. 生物信息入门到精通必修基础课:
linux系统使用
、
perl入门到精通
、
perl语言高级
、
R语言入门
、
R语言画图
7. 医学相关数据挖掘课程,不用做实验也能发文章:
TCGA-差异基因分析
、
GEO芯片数据挖掘
、
GEO芯片数据标准化
、
GSEA富集分析课程
、
TCGA临床数据生存分析
、
TCGA-转录因子分析
、
TCGA-ceRNA调控网络分析
8.其他,
二代测序转录组数据自主分析
、
NCBI数据上传
、
二代测序数据解读